林章凛教授课题组在ACS Synthetic Biology杂志上发表论文— 谷氨酸棒杆菌基因组合成大片段DNA迭代替换
基因组的合理设计与合成可加深我们对基因组结构、功能和进化的理解。目前已成功构建生殖支原体、大肠杆菌、酿酒酵母的合成基因组。谷氨酸棒状杆菌是公认安全(GRAS)的重要微生物细胞工厂,对其进行基因组合成将有助于更好地设计和改造菌种,但其基因组合成存在基因重叠较多、大片段导入困难、重组(替换)效率低等障碍进展缓慢。近日,作为谷氨酸棒状杆菌全基因组合成的预研实验,华南理工大学生物科学与工程学院林章凛课题组的叶燕锐副教授和华大生命科学研究院沈玥课题组的王云博士等通过RecE/RecT介导的同源重组方法将53.4 kb原始菌株基因组替换为了55.1 kb合成基因组,文章发表于ACS Synthetic Biology题为:Genomic Iterative Replacements of Large Synthetic DNA Fragments in Corynebacterium glutamicum。
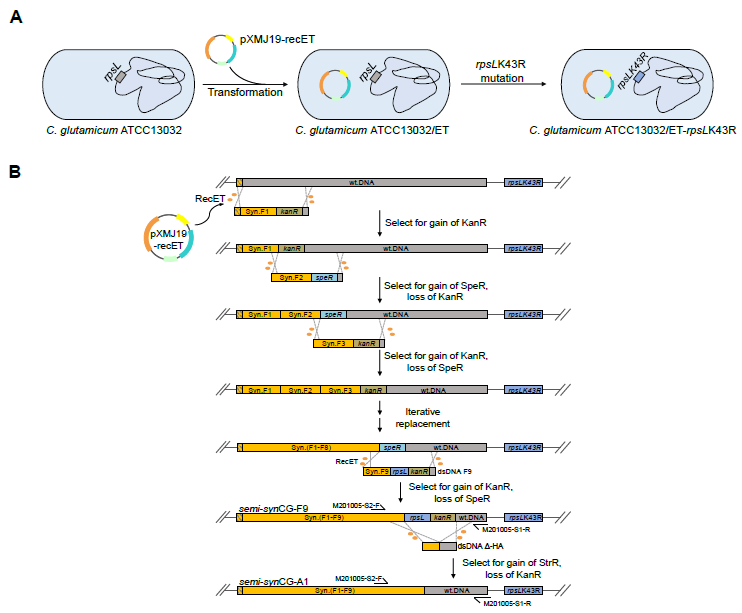
研究者以谷氨酸棒状杆菌ATCC 13032 为研究对象,选取了54.3 kb 基因组区域(3,156,174 – 3,210,459,无插入序列元件) 为目标替换序列。合成基因组参照酵母合成基因组计划:1. 接近野生型的表现型和适应性; 2. 缺乏破坏稳定的因素;3. 具有遗传灵活性,以促进未来的研究。遵循此原则,研究者重设计目标基因组:1. 将目标区域内的重叠基因进行解耦;2. 为提高基因组的灵活性,将所有TAG 更改为TAA 释放了一个密码子,并在20个终止密码子3 bp 后插入了loxPsym位点;3. 为区别合成型序列和野生型序列,引入了80对PCRTags作为DNA水印。相对于野生型序列,重新设计的基因组序列有27个插入点(共855 bp)和849个单核苷酸替换点,合成的序列被打断为4-9 kb的片段,并在每个片段后添加了卡那霉素或壮观霉素抗性基因和一个500 bp的同源臂序列,最终化学合成的序列长度为55,141 bp。
为最终获得无抗性的合成基因组,研究者将谷氨酸棒状杆菌ATCC 13032 编码核糖体蛋白S12的rpsL基因突变为rpsLK43R,使其具有链霉素抗性,当存在另一拷贝野生型rpsL时,会丧失链霉素抗性,并在合成基因组最后一个片段上添加rpsL,通过链霉素反筛获得无抗菌株。
目前,已报道3 对重组酶在谷氨酸棒状杆菌中可正常行使功能,其中 RecE/RecT 重组效率最高。研究者通过质粒引入RecE/RecT 重组酶,通过每个片段所携带的抗性对正确重组的菌株进行筛选,迭代将原始基因组替换为合成的基因组,最后再通过链霉素反筛获得了最终无标记的55.1 kb 基因组替换的谷氨酸棒状杆菌(原理如图)。
通过PCRTags对每一次重组的效率进行计算,正确的重组率在1%-14%,最大替换长度为10 kb。经测试,替换后的谷氨酸棒状杆菌可在无抗培养基稳定传代超100代,其表型在所测试的生长条件下(酸、碱、氧胁迫)生长状况均相同,只有在1 M NaCl 情况下基因组替换的菌株生长状态更优。最后,研究者通过诱导4 h或8 h表达重组酶,验证了所插入loxPsym位点可实现基因组缺失(30 kb)、倒位和易位,体现了合成型谷氨酸棒状杆菌基因组的遗传可塑性。
综上,本文建立了一种基于同源重组的谷氨酸棒状杆菌基因组迭代替换方法,为谷氨酸棒状杆菌的基因组合成和代谢工程研究提供了新思路。
该研究得到了国家重点研发专项(2017YFC1601202)等项目的支持。
版权与免责声明:本网页的内容由收集互联网上公开发布的信息整理获得。目的在于传递信息及分享,并不意味着赞同其观点或证实其真实性,也不构成其他建议。仅提供交流平台,不为其版权负责。如涉及侵权,请联系我们及时修改或删除。邮箱:sales@allpeptide.com