杜红丽教授课题组在Computational and Structural Biotechnology Journal杂志上在线发表论文——实时监测新冠病毒进化的自动化工具
近日,华南理工大学生物科学与工程学院杜红丽教授课题组在Computational and Structural Biotechnology Journal杂志上在线发表题为AutoVEM: an automated tool to real-time monitor epidemic trends and key mutations in SARS-CoV-2 evolution的研究论文。生物科学与工程学院本科生席彬彬为论文第一作者,博士研究生姜大伟为论文共同第一作者,杜红丽教授为通讯作者(论文链接https://www.sciencedirect.com/science/article/pii/S2001037021001082#s0005)。
目前,大多数针对SARS-CoV-2基因组进化或突变株分析鉴定的研究都采用构建系统进化树或针对单点突变分析的方法。然而,构建系统进化树耗时耗力,对单点突变分析则很难全局鉴定新冠突变株并实时监测。研究团队提出了一种联合病毒高频突变位点筛选、连锁分析和单倍型亚型分型及单倍亚型流行趋势分析从而鉴定SARS-CoV-2关键突变和突变株的新方法,并将整个流程开发成自动化分析工具(AutoVEM,图1)。该工具在1核CPU和2GB RAM的计算机上,18小时内分析完131,576 条SARS-CoV-2基因组序列(GISAID数据库,截止到2020年12月)。相对于该课题组之前采用构建系统进化树的方法,该方法效率提高了200倍以上,而且可以准确鉴定出随时间变化的关键突变及单倍亚型。分析数据显示,该课题组先前研究发现的9个突变位点(Comprehensive evolution and molecular characteristics of a large number of SARS-CoV-2 genomes reveal its epidemic trends,INT J INFECT DIS, 100 (2020):164-173)中的C241T、C3037T、C14408T、A23403G四个位点(H1单倍型)基本已在病毒群体中固定下来,占群体的70%以上,而其余5个突变位点则随着病毒的进化而消失。除此之外,团队还新发现了6个高度连锁的、可能影响SARS-CoV-2传染能力等的关键突变位点(T445C, C6286T, C22227T, G25563T, C26801G and G29645T)。
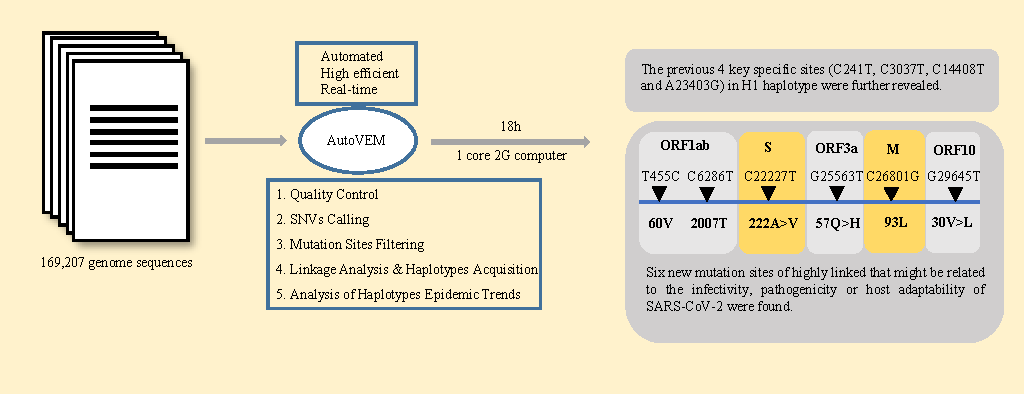

图1 AutoVEM工作流程图
该课题组在2020年初开始,从新冠病毒防控角度出发,开展了一系列新冠病毒相关的研究,并取得一定的成效。其中,先前的研究(Bai Y, et al. INT J INFECT DIS, 100 (2020): 164-173)受到科技部和WHO(2021年01月14日-2021年02月10日)报告引用以及外媒关注。而AutoVEM是在新冠病毒已全球流行,其突变很难阻止的背景下开发的。目的是为全球提供一个可以随时随地对本地或公共数据进行实时分析、实时监测新冠病毒关键突变位点和鉴定新流行突变株的自动化工具,从而为新冠疫苗研发及检测方法的发展更新提供参考,也为全球抗疫贡献一份力量。
该项工作得到国家重点研发计划(2018YFC0910201)和广东省重点研发计划(2019B020226001)等项目资助。
版权与免责声明:本网页的内容由收集互联网上公开发布的信息整理获得。目的在于传递信息及分享,并不意味着赞同其观点或证实其真实性,也不构成其他建议。仅提供交流平台,不为其版权负责。如涉及侵权,请联系我们及时修改或删除。邮箱:sales@allpeptide.com